偃松乙酰辅酶A羧化酶β-CT亚基基因生物信息学分析
【类型】期刊
【作者】林琳,张状,李雪莲,侯炳柱,李琢,夏富才(北华大学林学院;吉林市龙潭区实验林场;吉林市龙潭区江密峰林场;珲春林业局三道沟林场)
【作者单位】北华大学林学院;吉林市龙潭区实验林场;吉林市龙潭区江密峰林场;珲春林业局三道沟林场
【刊名】北华大学学报(自然科学版)
【关键词】 偃松;乙酰辅酶A羧化酶;生物信息学
【资助项】科技部国家重点研发计划项目(2017YFC0504102);北华大学博士科研启动基金项目
【ISSN号】1009-4822
【页码】P307-311
【年份】2019
【期号】第3期
【期刊卷】7;|4
【摘要】乙酰辅酶A羧化酶是脂肪酸合成的关键酶,其β-CT亚基由质体基因组中的accD基因编码.利用生物信息学分析偃松accD基因序列,为进一步研究accD基因功能提供参考.结果显示:偃松accD基因序列长度为428 bp,与不丹松、白皮松、台湾五针松和红松相似度高达100%;accD基因系统发育树表明,偃松与日本白松和红松聚为一个类群;accD基因编码的β-CT蛋白由11种氨基酸组成,有1个跨膜结构域,是亲水性较强的蛋白.
【全文】 文献传递
偃松乙酰辅酶A羧化酶β-CT亚基基因生物信息学分析
摘要:乙酰辅酶A羧化酶是脂肪酸合成的关键酶,其β-CT亚基由质体基因组中的accD基因编码.利用生物信息学分析偃松accD基因序列,为进一步研究accD基因功能提供参考.结果显示:偃松accD基因序列长度为428 bp,与不丹松、白皮松、台湾五针松和红松相似度高达100%;accD基因系统发育树表明,偃松与日本白松和红松聚为一个类群;accD基因编码的β-CT蛋白由11种氨基酸组成,有1个跨膜结构域,是亲水性较强的蛋白.
关键词:偃松;乙酰辅酶A羧化酶;生物信息学
偃松(Pinus pumila)为松科(Pinaceae)灌木状小乔木,主要分布在大兴安岭、小兴安岭、张广才岭、老爷岭、长白山等地海拔1 000 m以上区域,是寒温带地区重要的坚果来源和潜在的木本油料植物[1].偃松种仁营养丰富,含油量高.其中,不饱和脂肪酸含量高达59.4%;油脂成分类似于杏油和橄榄油,可用于食品、医药及化妆品行业[2-3].
乙酰辅酶A羧化酶(acetyl-CoA carboxylase,ACCase)是脂肪酸合成的关键酶.在植物中,乙酰辅酶A羧化酶主要有异质型和同质型两种.异质型ACCase由生物素羧基载体蛋白(biotin carboxyl carrier protein,BCCP)亚基、生物素羧化酶(biotin carboxylase,BC)亚基、羧基转移酶(carboxyl transferase,CT)的α-CT亚基和β-CT亚基等4种亚基组成,参与脂肪酸的合成[4-5].其中,α-CT亚基、BCCP亚基和BC亚基分别由核基因accA,accB和accC编码;β-CT亚基由质体基因组中的accD编码[6].异质型ACCase是植物种子脂肪酸合成的关键酶,与种子含油量密切相关[7].其中,β-CT亚基是异质型ACCase的限制因子,在植物ACCase活性和植物种子含油量中起重要作用[8].近年来,随着对β-CT亚基研究的不断深入,人们已从苜蓿(Medicago truncatula)、石栗(Aleurites moluccana)、油棕(Elaeis guineensis)等多种农作物和木本植物中克隆到β-CT亚基的编码基因accD[9-11].由于特有的生命周期长,基因组结构复杂,遗传操作困难等生物学特性,有关针叶树accD基因的研究还未见报道.因此,笔者利用生物信息学方法对偃松accD基因的核酸/蛋白质序列分子特征、一级结构、二级结构以及三维结构进行预测,并对该基因进行系统进化分析,从而为针叶树accD基因的克隆和功能验证提供理论和实践参考.
1 材料及方法
1.1 材 料
参照NCBI(https://www.ncbi.nlm.nih.gov)数据库中已报道的偃松(P.pumila,EF523978.1)、奄美松(P.amamiana,JN854226.1)、台湾五针松(P.morrisonicola,JN854182.1)、不丹松(P.wallichiana,JN854154.1)、白皮松(P.bungeana,JN854223.1)、西伯利亚红松(P.sibirica,KT723438.2)、日本白松(P.parviflora,EF523979.1)、红松(P.koraiensis,EF523977.1)、华南五针松(P.kwangtungensis,JN854153.1)、华山松(P.armandii,KP412541.1)、北美乔松(P.strobus,FJ899560.1)、高山松(P.densata,JN854209.1)、火炬松(P.taeda,KC427273.1)accD基因的mRNA序列以及相应的氨基酸序列.
1.2 方 法
利用NCBI对偃松accD基因进行BLAST(https://blast.ncbi.nlm.nih.gov/Blast.cgi)比对,使用ORFFinder(https://www.ncbi.nlm.nih.gov/genbank)进行开放阅读框分析;使用ProtParam(http://web.expasy.org/protparam)分析偃松乙酰辅酶A羧化酶β-CT亚基氨基酸序列的相对分子质量、碱基分布和氨基酸组成;利用Protscale(http://web.expasy.org/protscale)预测亲疏水性;利用SignnalP-4.1(http://www.cbs.dtu.dk/services/SignalP)进行信号肽预测;使用TMHMM Server v.2.0(http://www.cbs.dtu.dk/services/TMHMM)分析氨基酸序列的跨膜结构域;使用SWISS-MODEL(https://swissmodel.expasy.org)进行同源建模,构建三维结构示意图;利用MEGA5(www.mega.co.nz)构建偃松等13个松属植物的accD基因序列同源进化树.
2 结果与分析
2.1 同源性
偃松乙酰辅酶A羧化酶β-CT亚基在Genbank中的登录号为EF523978.1.根据登录号进行BLAST,发现在松属植物中共有29条序列与偃松乙酰辅酶A羧化酶β-CT亚基的氨基酸序列相似.其中,不丹松、白皮松、台湾五针松和红松与偃松accD基因的相似度高达100%(见图1).
2.2 开放阅读框
利用ORFFinder对偃松accD基因进行开放阅读框分析,获得1条长428 bp的开放阅读框,起始密码子位于1 bp,终止密码子位于428 bp.共得到3个ORF,其中,ORF1起始于136位,结束于219位;ORF2起始于308位,结束于>427位;ORF3起始于239位,结束于144位.该核苷酸序列是一个无打断的碱基序列,序列中间不存在终止密码子,可完整编码相应蛋白(见图2).
2.3 氨基酸组成
ProtParam分析表明,偃松乙酰辅酶A羧化酶β-CT亚基的分子式为C213H344N44O48S2,相对分子质量为4 353.46,共含有11种氨基酸.其中,亮氨酸的比例最高,占所有氨基酸的25%,其后依次为色氨酸(20%)、异亮氨酸(12.5%)、天冬氨酸(10%)、缬氨酸(7.5%)、苯丙氨酸(7.5%)、丝氨酸(5%)、蛋氨酸(5%)、丙氨酸(2.5%)、甘氨酸(2.5%)、苏氨酸(2.5%).不稳定指数为79.13,为不稳定蛋白质(见图3).

图1 偃松accD基因的BLAST比对结果
Fig.1 BLAST comparison of accD gene in Pinus pumila
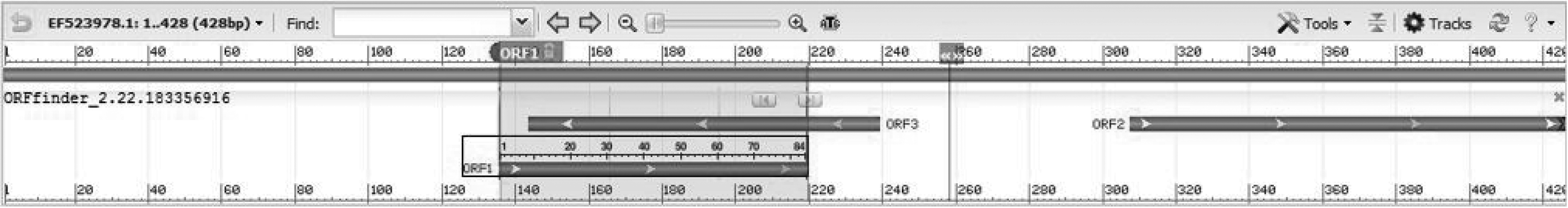
图2 偃松accD基因的开放阅读框分析
Fig.2 Open reading frame of accD gene in Pinus pumila
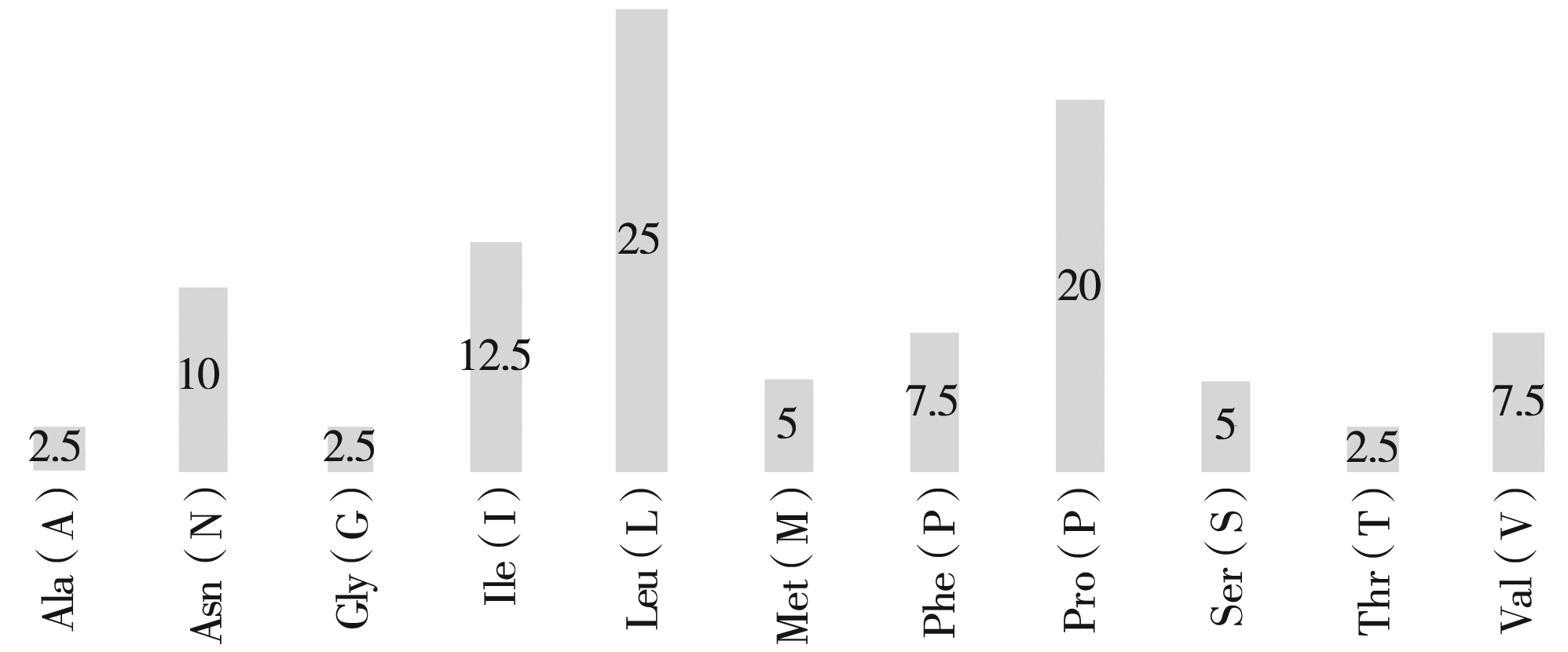
图3 偃松乙酰辅酶A羧化酶β-CT亚基蛋白质氨基酸组成
Fig.3 Amino acid composition of acetyl-CoA carboxylase β-CT subunit in Pinus pumila
2.4 蛋白质亲疏水性
组成偃松乙酰辅酶A羧化酶β-CT亚基的氨基酸分子具有一定极性,这些极性氨基酸对蛋白质高级结构的形成具有重要影响.Protscale分析结果表明,该基因编码的氨基酸有50%以上得分为正值,说明该蛋白为亲水性蛋白.其中,最高得分为1.9,出现在350 bp;最低得分为-0.4,出现在20,235和380 bp(见图4).
2.5 信号肽预测
在起始密码子后有一段疏水性氨基酸序列,负责把蛋白质引导到不同膜结构的亚细胞器内,这段氨基酸序列被称为信号肽序列.利用SignalP-4.1分析偃松乙酰辅酶A羧化酶β-CT亚基发现,C的最大值为0.105,出现在第35个氨基酸上;Y的最大值为0.164,出现在第5个氨基酸上;S的最大值为0.255,出现在第2个氨基酸上(见图5).由此可知,该基因序列分值较低且没有信号肽剪切位点,因此不具有信号肽,说明该蛋白质不属于分泌蛋白.
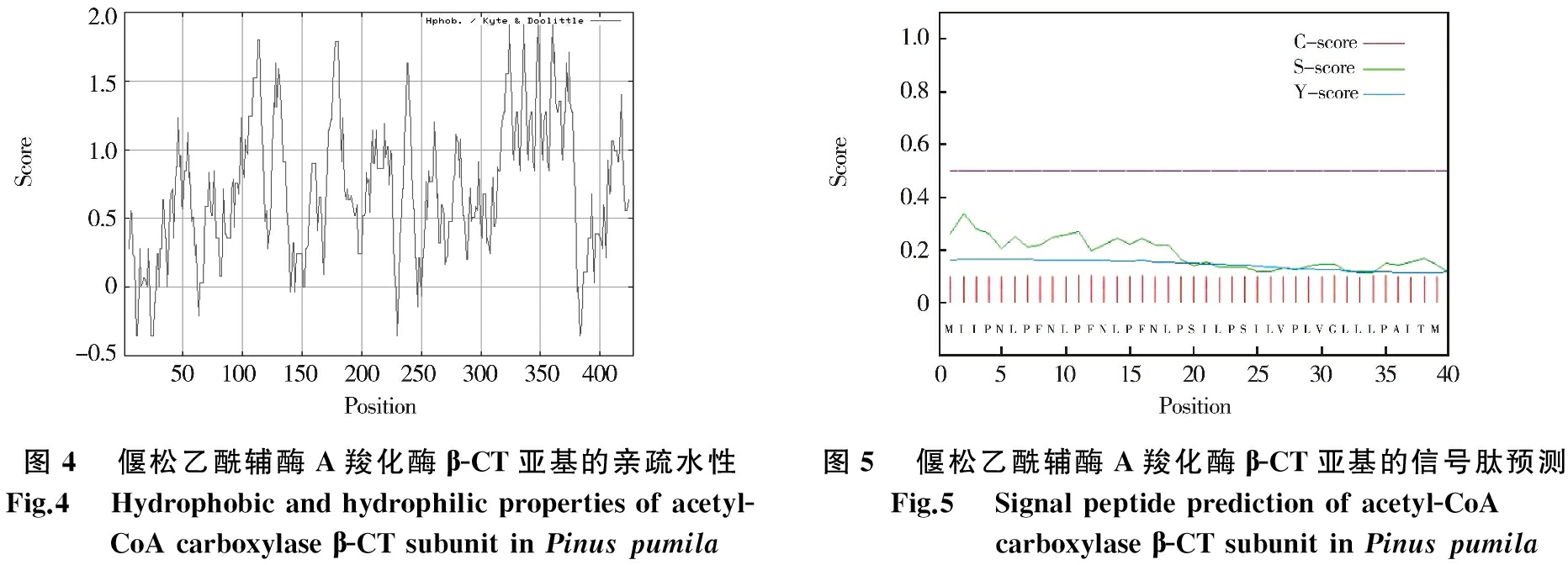
图4偃松乙酰辅酶A羧化酶β-CT亚基的亲疏水性Fig.4Hydrophobicandhydrophilicpropertiesofacetyl-CoAcarboxylaseβ-CTsubunitinPinuspumila图5偃松乙酰辅酶A羧化酶β-CT亚基的信号肽预测Fig.5Signalpeptidepredictionofacetyl-CoAcarboxylaseβ-CTsubunitinPinuspumila
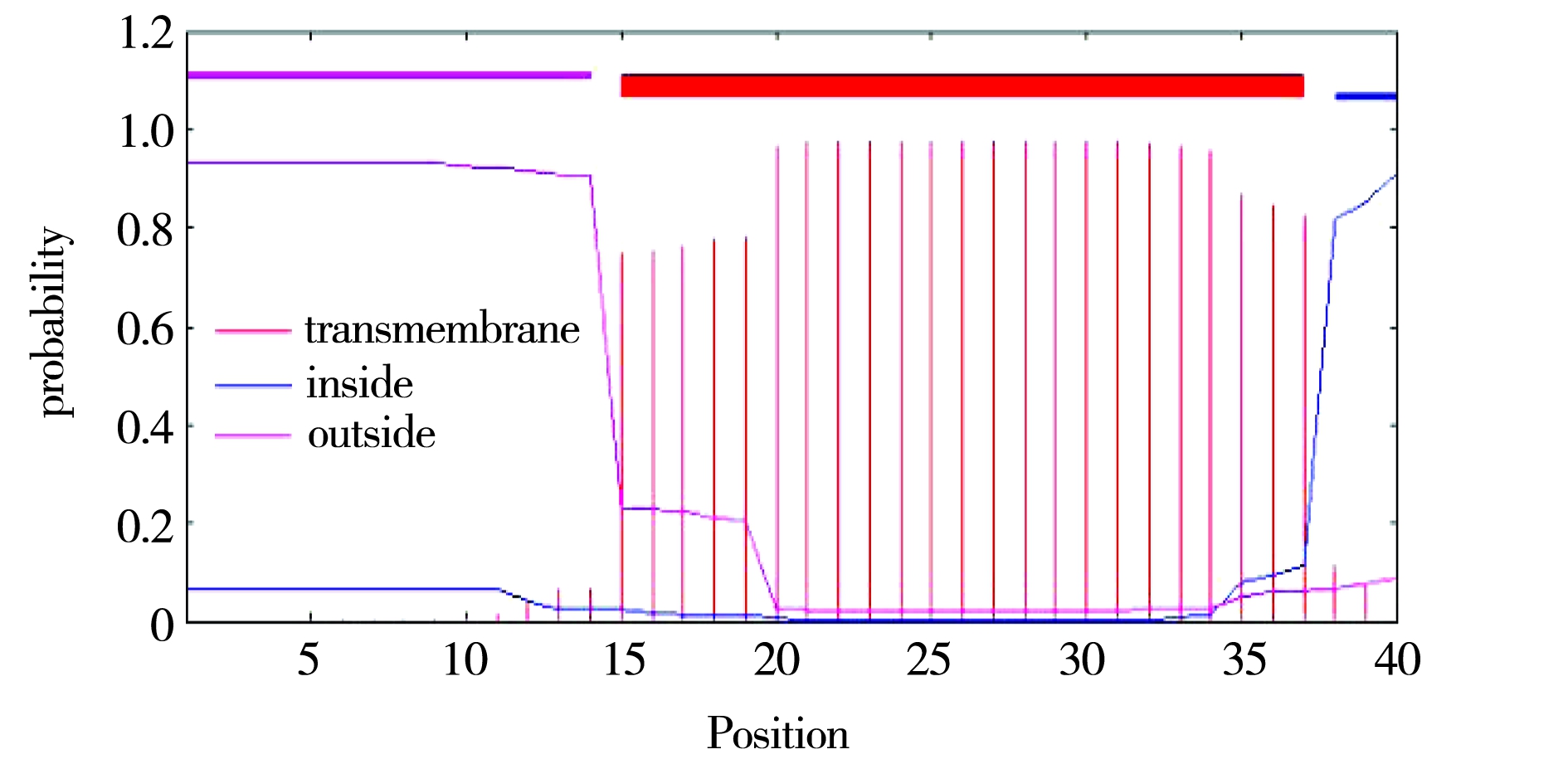
图6 偃松乙酰辅酶A羧化酶β-CT亚基的跨膜结构
Fig.6 Transmembrane domain of acetyl-CoA carbox- ylase β-CT subunit in Pinus pumila
2.6 蛋白质跨膜区
蛋白质跨膜区连接细胞内、外,主要功能是固定和介导信号传递.TMHMM Server v.2.0分析表明,偃松乙酰辅酶A羧化酶β-CT亚基有1个跨膜结构域,多肽链1~14位于膜外,15~37横跨质膜,38~40位于膜内(见图6),由此可推断,偃松乙酰辅酶A羧化酶β-CT亚基在质膜上发挥功能.
2.7 蛋白质三维结构
利用SWISS-MODEL中的自动方式(automated mode)进行同源建模,预测偃松乙酰辅酶A羧化酶β-CT亚基的三维结构.结果发现,该蛋白主要由螺旋结构和链状结构组成,其中,螺旋结构大约占75%(见图7).
2.8 系统进化树构建
利用MEGA5构建偃松accD基因的系统进化树,发现该进化树主要分为两个类群.其中,偃松与日本白松、红松聚为一个类群(见图8),说明偃松、日本白松和红松的accD基因亲缘性较近,这可能与这3个树种的地理分布区相似有关.

图7偃松乙酰辅酶A羧化酶β-CT亚基的三维结构Fig.7Three-dimensionalstructureofacetyl-CoAcar-boxylaseβ-CTsubunitinPinuspumila图8偃松accD基因的系统进化树Fig.8PhylogenetictreeaccDgeneinPinuspumila
3 结论与讨论
乙酰辅酶A羧化酶是催化种子脂肪酸合成最关键的限速酶.大量研究表明,乙酰辅酶A羧化酶的 BCCP,BC,α-CT和β-CT亚基中任何一个亚基基因的过量表达均可提高种子的含油率[12-13].植物中β-CT亚基由质体基因accD编码,在叶绿体中与α-CT亚基的前体蛋白结合,形成乙酰辅酶A羧化酶三大功能结构域之一的羧基转移酶[14].本次研究在NCBI中找到了偃松accD基因序列,该序列长428 bp,与不丹松、白皮松、台湾五针松和红松的相似度高达100%;accD基因系统发育树表明,偃松与日本白松和红松聚为一个类群;编码的蛋白质含有11种氨基酸,为亲水性蛋白,在质膜上发挥功能.以上研究结果可为今后深入研究偃松accD基因及通过基因工程进行遗传改良提供参考.
参考文献:
[1] 谭洪涛.偃松的分布及保护利用价值[J].内蒙古林业调查设计,2013,36(5):27,30.
[2] 赵垦田,李玉昌,张桂玲.大兴安岭偃松林资源及其开发利用与保护[J].国土与自然资源研究,1997(2):55-59.
[3] 谢振东.浅论内蒙古大兴安岭偃松矮曲林的价值[J].内蒙古林业调查设计,1999,22(3):117-119.
[4] 谭晓风,蒋瑶,王保明,等.油茶乙酰辅酶A羧化酶BC亚基全长cDNA克隆及序列分析[J].中南林业科技大学学报,2010,30(2):1-9.
[5] Xuan X Y,Zhang Y,Liu Z Q,et al.Molecular cloning and expression analysis of a novel BCCP subunit gene from Aleurites moluccana[J].Genetics and Molecular Research,2015,14(3):9922-9931.
[6] 王哲,谭晓风,龙洪旭.油桐乙酰辅酶A羧化酶BC亚基全长cDNA克隆及序列分析[J].中南林业科技大学学报,2015,35(3):53-58.
[7] 王哲,谭晓风,龙洪旭,等.油桐异质型乙酰辅酶A羧化酶accA亚基全长cDNA克隆及序列分析[J].经济林研究,2014,32(3):1-7.
[8] Rousseau-Gueutin M,Huang X,Higginson E,et al.Potential functional replacement of the plastidic acetyl-CoA carboxylase subunit (accD) gene by recent transfers to the nucleus in some angiosperm lineages[J].Plant Physiology,2013,161(4):1918-1929.
[9] Nakkaew A,Chotigeat W,Eksomtramage T,et al.Cloning and expression of a plastid-encoded subunit,β-carboxyltransferase gene (accD) and a nuclear-encoded subunit,biotin carboxylase of acetyl-CoA carboxylase from oil palm (Elaeis guineensis Jacq.)[J].Plant Science,2008,175(4):497-504.
[10] 王磊.石栗种子内含物变化及accD基因的克隆研究[D].南宁:广西大学,2013.
[11] Gurdon C,Maliga P.Two distinct plastid genome configurations and unprecedented intraspecies length variation in the accD coding region in Medicago truncatula[J].DNA Research,2014,21(4):417-427.
[12] Ohlrogge.Methods of increasing oil content of seeds[J].United States Patent,1999,925(5):805.
[13] Sasaki Y,Nagano Y.Plant acetyl-CoA carboxylase:structure,biosynthesis,regulation,and gene manipulation for plant breeding[J].Bioscience,Biotechnology,and Biochemistry,2004,68(6):1175-1184.
[14] Tran T H,Hsiao Y S,Jo J,et al.Structure and function of a single-chain,multi-domain long-chain acyl-CoA carboxylase[J].Nature,2015,518(7537):120-124.
Bioinformatics Analysis of Acetyl-CoA Carboxylase β-CTSubunit Gene in Pinus pumila
Abstract: Acetyl-CoA carboxylase is a key enzyme in fatty acid biosynthesis,and its β-CT subunit is encoded by the accD gene in the plastid genome.It provides a reference for further study of the accD gene function to make bioinformatics analysis of accD gene in Pinus pumila.The length of acquired sequence was 428 bp.Compared with accD mRNA in P.wallichiana,P.bungeana,P.morrisonicola and P.koraiensis,the resemblance was 100%.P.pumila,P.parviflora and P.koraiensis were clustered into one taxon in phylogenetic trees of accD gene.The β-CT protein encoded by accD gene included 11 kinds of amino acids,with a transmembrane domain and was a hydrophilic protein.
Key words: Pinus pumila;acetyl-CoA carboxylase;bioinformatics
文章编号:1009-4822(2018)03-0307-05
DOI:10.11713/j.issn.1009-4822.2018.03.005
中图分类号:S718.46
文献标志码:A
收稿日期:2018-03-03
基金项目:科技部国家重点研发计划项目(2017YFC0504102);北华大学博士科研启动基金项目.
【责任编辑:郭 伟】

